Wybierz wielkość
| Gabaryty przesyłki | SKU | Dostępność | Cena netto |
|---|---|---|---|
| 100 μL | Przewidywany termin wysyłki27 maja 2026zKuehne + Nagel Sp. z o.o. | 2370,00 zł |
Informacje o tej pozycji
biological source
rabbit
Quality Segment
antibody form
culture supernatant
antibody product type
primary antibodies
clone
AW30, monoclonal
species reactivity
chicken, human
manufacturer/tradename
Upstate®
technique(s)
ChIP: suitable (ChIP-seq), dot blot: suitable, inhibition assay: suitable (peptide), western blot: suitable
isotype
IgG
NCBI accession no.
UniProt accession no.
shipped in
dry ice
target post-translational modification
dimethylation (Lys4)
Gene Information
human ... H3C1(8350)
General description
Immunogen
Application
Rozcieńczenie 1:1000-1:2000 tej partii wykryło dimetyl histonu H3 (Lys4) w ekstraktach kwasu HeLa.
Analiza Western Blot:
Rozcieńczenie 1:2,000 do 1:10,000 poprzedniej partii wykryło metylowany histon H3 w białkach ekstrahowanych kwasem z komórek HeLa. Przeciwciało nie wykryło niemetylowanego rekombinowanego histonu H3.
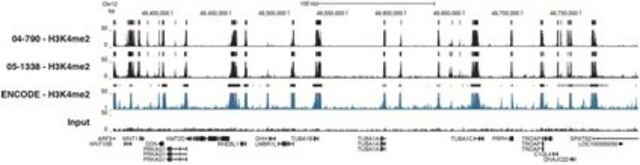
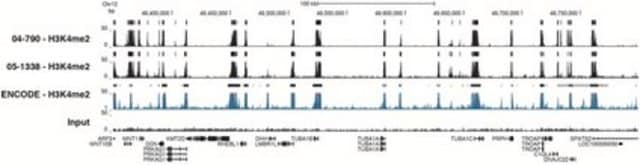
Analiza ChIP-seq:
Reprezentatywne dane partii. Immunoprecypitację chromatyny przeprowadzono przy użyciu zestawu Magna ChIP HiSens (nr kat. 17-10460), przeciwciała przeciw dimetylowi-histonowi H3 (Lys4) (2 µl nr kat. 04-790), 20 µl kulek Protein A/G i 1e6 usieciowanej chromatyny komórek HeLa, a następnie oczyszczono DNA za pomocą kulek magnetycznych. Biblioteki zostały przygotowane z próbek Input i ChIP DNA przy użyciu standardowych protokołów z adapterami Illumina z kodem kreskowym i analizowane na instrumencie Illumina HiSeq. Ponad szesnaście milionów odczytów z plików FastQ zmapowano za pomocą Bowtie (http://bowtie-bio.sourceforge.net/manual.shtml) po usunięciu tagów TagDust (http://genome.gsc.riken.jp/osc/english/dataresource/). Piki zostały zidentyfikowane przy użyciu MACS (http://luelab.dfci.harvard.edu/MACS/), z pikami i odczytami wizualizowanymi jako niestandardowa ścieżka w UCSC Genome Browser (http://genome.ucsc.edu) z plików BigWig i BED. Najwyższe 25% pików zidentyfikowanych w zbiorach danych 04-790 i 05-1338 wykazało 92 i 90% pokrywania się z pikami zidentyfikowanymi w ścieżce ENCODE H3K4me2 BROAD Histone dla HeLa S3.
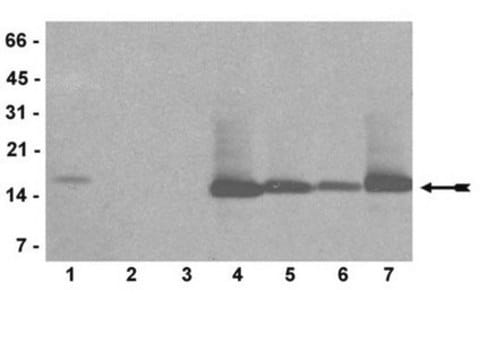
Analiza Dot Blot:
Absurance Histone H3 Antibody Specificity Array (nr kat. 16-667) i Absurance Histone H2A, H2B, H4 Antibody Specificity Array (nr kat. 16-665), które zawierają peptydy histonowe z różnymi modyfikacjami, były sondowane z Cat. 04-790, Anti-dimethyl Histone H3 (Lys4), klon AW30 w rozcieńczeniu 1:1000. Białka były wizualizowane przy użyciu IgG Osioł anty-Rabbit sprzężonej z HRP i systemu detekcji chemiluminescencji.
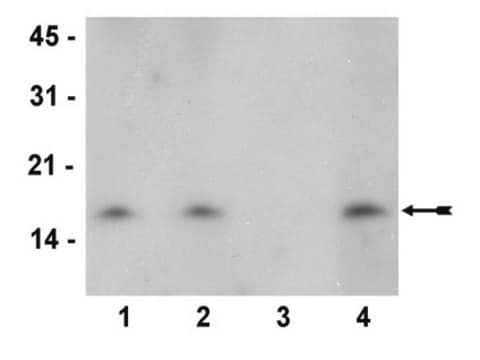
Analiza inhibicji peptydowej:
2 μM peptydu histonu H3 zawierającego dimetylo-lizynę 4 zniosło wykrywanie histonu H3 przez poprzednią partię przeciwciał w analizie immunoblot ekstraktów kwasu HeLa. Nie zaobserwowano redukcji sygnału w przypadku peptydów histonu H3 zawierających modyfikacje monometylo- lub trimetylo-lizyny 4
Epigenetyka i funkcje jądrowe
Histony
Biochem/physiol Actions
Physical form
Preparation Note
Aby uzyskać maksymalny odzysk produktu, należy odwirować fiolkę przed zdjęciem nasadki.
Analysis Note
Ekstrakty kwasu HeLa
Other Notes
Legal Information
Disclaimer
1 of 1
Ta pozycja | |||
|---|---|---|---|
| clone AW30, monoclonal | clone AW30, monoclonal | clone AW304, monoclonal | clone 614M, monoclonal |
| Gene Information human ... H3C1(8350) | Gene Information human ... H3C1(8350) | Gene Information human ... H3C1(8350) | Gene Information human ... H3C1(8350) |
| biological source rabbit | biological source rabbit | biological source rabbit | biological source rabbit |
| species reactivity chicken, human | species reactivity human, chicken | species reactivity vertebrates, human | species reactivity vertebrates |
| antibody form culture supernatant | antibody form culture supernatant | antibody form culture supernatant | antibody form culture supernatant |
| UniProt accession no. | UniProt accession no. | UniProt accession no. | UniProt accession no. |
Still not finding the right product?
Wypróbuj nasze narzędzie Narzędzie selektora produktów, aby zawęzić opcje.
Klasa składowania
12 - Non Combustible Liquids
wgk
WGK 1
flash_point_f
Not applicable
flash_point_c
Not applicable
Certyfikaty analizy (CoA)
Poszukaj Certyfikaty analizy (CoA), wpisując numer partii/serii produktów. Numery serii i partii można znaleźć na etykiecie produktu po słowach „seria” lub „partia”.
Masz już ten produkt?
Dokumenty związane z niedawno zakupionymi produktami zostały zamieszczone w Bibliotece dokumentów.
Powiązane treści
Cancer is a complex disease manifestation. At its core, it remains a disease of abnormal cellular proliferation and inappropriate gene expression. In the early days, carcinogenesis was viewed simply as resulting from a collection of genetic mutations that altered the gene expression of key oncogenic genes or tumor suppressor genes leading to uncontrolled growth and disease (Virani, S et al 2012). Today, however, research is showing that carcinogenesis results from the successive accumulation of heritable genetic and epigenetic changes. Moreover, the success in how we predict, treat and overcome cancer will likely involve not only understanding the consequences of direct genetic changes that can cause cancer, but also how the epigenetic and environmental changes cause cancer (Johnson C et al 2015; Waldmann T et al 2013). Epigenetics is the study of heritable gene expression as it relates to changes in DNA structure that are not tied to changes in DNA sequence but, instead, are tied to how the nucleic acid material is read or processed via the myriad of protein-protein, protein-nucleic acid, and nucleic acid-nucleic acid interactions that ultimately manifest themselves into a specific expression phenotype (Ngai SC et al 2012, Johnson C et al 2015). This review will discuss some of the principal aspects of epigenetic research and how they relate to our current understanding of carcinogenesis. Because epigenetics affects phenotype and changes in epigenetics are thought to be key to environmental adaptability and thus may in fact be reversed or manipulated, understanding the integration of experimental and epidemiologic science surrounding cancer and its many manifestations should lead to more effective cancer prognostics as well as treatments (Virani S et al 2012).
Numer pozycji handlu globalnego
| SKU | NUMER GTIN |
|---|---|
| 04-790 | 04053252513107 |