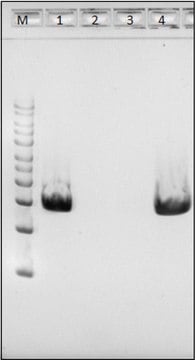
Wszystkie zdjęcia(3)
Kluczowe dokumenty
MBD6000
5R-Plex kit
Ultra-sensitive 16S NGS assay for degraded and low biomass DNA
Zaloguj sięWyświetlanie cen organizacyjnych i kontraktowych
About This Item
Kod UNSPSC:
41106302
NACRES:
NA.84
Polecane produkty
Poziom jakości
zastosowanie
Preparing 96 samples for sequencing
metody
DNA amplification: suitable
DNA sequencing: suitable
Warunki transportu
dry ice
temp. przechowywania
-10 to -25°C
Opis ogólny
The 16S ribosomal RNA gene (16S rRNA) is a common bacterial marker, used as a target for microbial community profiling in microbiome metagenomic studies. The gene is composed of nine variable regions (V1-V9) interspersed between conserved regions. The most common 16S rRNA NGS assays target one or two regions using a single set of primers (e.g., V3-V4). However, this approach usually results in a poor bacterial detection and classification rate when the DNA input is of low-quality or when applying it on extremely low biomass samples. The 5R-PLEX kit offers a complete solution to challenging biological samples where the standard 16S sequencing protocols fail to perform. Sample types include:
- Formalin-Fixed, Paraffin-Embedded (FFPE) tissue
- Cancerous tumor tissue
- Degraded or damaged DNA
- Low biomass samples
- Fossil-derived and ancient DNA
Cechy i korzyści
- The 5R-PLEX Kit provides high profile sequencing from degraded, damaged or low biomass samples
- Multiplexed NGS assay targets 5 variable regions of the 16S rRNA gene in a single primer pool
- Includes positive control for trouble shooting experiments.
- The kit can detect as low as 1pg of highly degraded bacterial DNA with an average fragment size of 260bp.
- Kit includes low bioburden reagents
- Includes exclusive access to M-CAMP™ platform featuring an innovative algorithm designed to reconstruct a single coherent microbial profiling and perform comprehensive analysis.
Komponenty
- 5R-PLEX PCR1 Primer mix- 25 μL
- 5R-PLEX PCR2 Forward Primer mix- 25 μL
- 5R-PLEX index plate 96-plate
- Water, microbial DNA-free 10X- 1.5 mL
- HF DNA Polymerase- 0.1 mL
- 5X HF buffer 2 mL
- dNTP′s- 0.2 mL
- Elution Buffer (EB), microbial DNA-free- 8 mL
- 5R-PLEX Positive Control (10 ng/μL)- 30 μL
Przechowywanie i stabilność
The shelf life of all reagents provided in the kit is 12 months when stored properly. Store all components at -20 °C.
Inne uwagi
Kit component details can be found in the User guide.
Informacje prawne
M-Camp is a trademark of Merck KGaA, Darmstadt, Germany
Ta strona może zawierać tekst przetłumaczony maszynowo.
Zwroty wskazujące rodzaj zagrożenia
Zwroty wskazujące środki ostrożności
Klasyfikacja zagrożeń
Aquatic Chronic 3
Kod klasy składowania
10 - Combustible liquids
Wybierz jedną z najnowszych wersji:
Certyfikaty analizy (CoA)
Lot/Batch Number
Nie widzisz odpowiedniej wersji?
Jeśli potrzebujesz konkretnej wersji, możesz wyszukać konkretny certyfikat według numeru partii lub serii.
Masz już ten produkt?
Dokumenty związane z niedawno zakupionymi produktami zostały zamieszczone w Bibliotece dokumentów.
Deborah Nejman et al.
Science (New York, N.Y.), 368(6494), 973-980 (2020-05-30)
Bacteria were first detected in human tumors more than 100 years ago, but the characterization of the tumor microbiome has remained challenging because of its low biomass. We undertook a comprehensive analysis of the tumor microbiome, studying 1526 tumors and
Garold Fuks et al.
Microbiome, 6(1), 17-17 (2018-01-28)
Most of our knowledge about the remarkable microbial diversity on Earth comes from sequencing the 16S rRNA gene. The use of next-generation sequencing methods has increased sample number and sequencing depth, but the read length of the most widely used
Amnon Amir et al.
Nucleic acids research, 41(22), e205-e205 (2013-11-12)
The emergence of massively parallel sequencing technology has revolutionized microbial profiling, allowing the unprecedented comparison of microbial diversity across time and space in a wide range of host-associated and environmental ecosystems. Although the high-throughput nature of such methods enables the
Jacob T Nearing et al.
Microbiome, 9(1), 113-113 (2021-05-20)
Advances in DNA sequencing technology have vastly improved the ability of researchers to explore the microbial inhabitants of the human body. Unfortunately, while these studies have uncovered the importance of these microbial communities to our health, they often do not
Nicole M Davis et al.
Microbiome, 6(1), 226-226 (2018-12-19)
The accuracy of microbial community surveys based on marker-gene and metagenomic sequencing (MGS) suffers from the presence of contaminants-DNA sequences not truly present in the sample. Contaminants come from various sources, including reagents. Appropriate laboratory practices can reduce contamination, but
Nasz zespół naukowców ma doświadczenie we wszystkich obszarach badań, w tym w naukach przyrodniczych, materiałoznawstwie, syntezie chemicznej, chromatografii, analityce i wielu innych dziedzinach.
Skontaktuj się z zespołem ds. pomocy technicznej